Розробка параметро-ефективного методу синтезу біомедичних зображень шляхом заміни текстового кондиціювання ембедінгами фундаментальної моделі патології у латентній дифузії
DOI:
https://doi.org/10.15587/2706-5448.2026.355663Ключові слова:
латентні дифузійні моделі, фундаментальні моделі патології, синтез гістопатологічних зображень, генерація медичних зображеньАнотація
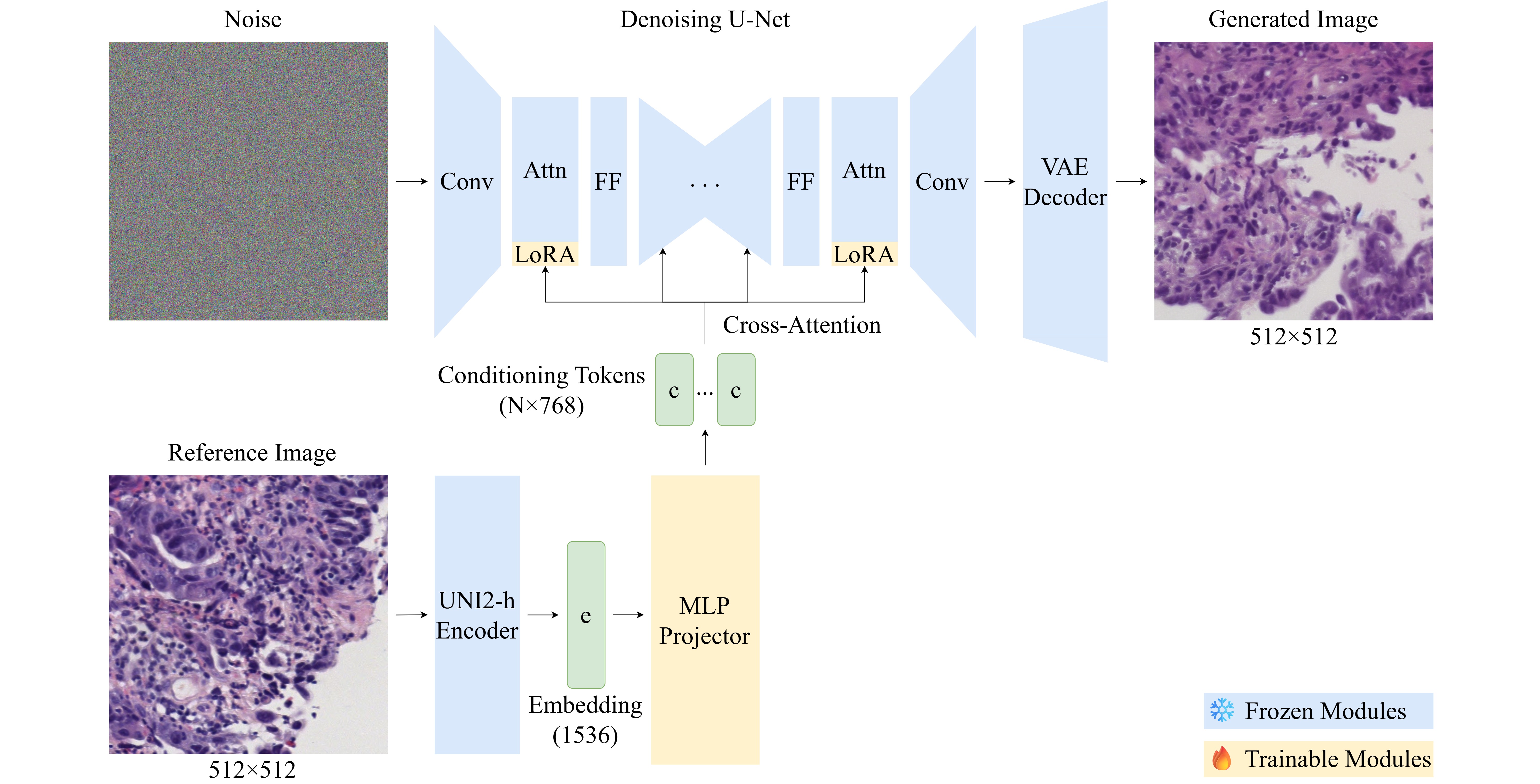
Об’єктом дослідження є процес синтезу патчів гістопатологічних зображень, кондиційованих ембедінгами фундаментальної моделі патології. Однією з ключових проблем є те, що наявні підходи до дифузійного синтезу або спираються на текстове кондиціювання через CLIP-енкодери, яким бракує морфологічного розуміння, або потребують повного донавчання генеративної базової моделі, що вимагає значних обчислювальних ресурсів.
У ході дослідження використовувалася параметроефективна адаптація попередньо навченої латентної дифузійної моделі з використанням низькорангової адаптації (LoRA) шарів уваги U-Net у поєднанні з навченим MLP-проєктором, який відображає ембедінги фундаментальної моделі патології UNI2-h у простір кондиціювання механізму перехресної уваги. Проведено абляційні дослідження 12 конфігурацій із варіюванням рангу адаптера, кількості токенів кондиціювання та архітектури проєктора.
Отримано підтвердження того, що ембедінги фундаментальної моделі патології можуть ефективно замінити текстове кондиціювання для синтезу гістопатологічних зображень у параметроефективному режимі. Оптимальна конфігурація досягла FID 77,59 на валідаційній вибірці та FID 84,17 на тестовій вибірці при навчанні лише 5,53 млн параметрів, що становить 0,64% параметрів базової моделі. Це зумовлено тим, що запропонований метод має низку характерних особливостей, зокрема: ембедінги фундаментальної моделі забезпечують морфологічно багатший сигнал кондиціювання, ніж текстові CLIP-представлення, а низькорангова адаптація обмежує простір навчуваних параметрів шляхом кондиціювання.
Завдяки цьому забезпечується можливість генерації гістопатологічних зображень без текстових анотацій та без повного донавчання моделі, використовуючи орієнтовно 12 ГБ відеопам’яті. Порівняно з попереднім текстово-кондиційованим підходом на тому самому наборі даних, який демонстрував покласові значення FID у діапазоні від 113 до 138, метод кондиціювання ембедінгами забезпечує істотно вищу якість генерації зі збереженням параметроефективності.
Посилання
- Litjens, G., Bandi, P., Ehteshami Bejnordi, B., Geessink, O., Balkenhol, M., Bult, P. et al. (2018). 1399 H&E-stained sentinel lymph node sections of breast cancer patients: the CAMELYON dataset. GigaScience, 7 (6). https://doi.org/10.1093/gigascience/giy065
- Walsh, E., Orsi, N. M. (2024). The current troubled state of the global pathology workforce: a concise review. Diagnostic Pathology, 19 (1). https://doi.org/10.1186/s13000-024-01590-2
- Guan, H., Yap, P.-T., Bozoki, A., Liu, M. (2024). Federated learning for medical image analysis: A survey. Pattern Recognition, 151, 110424. https://doi.org/10.1016/j.patcog.2024.110424
- Zhang, Y., Kang, B., Hooi, B., Yan, S., Feng, J. (2023). Deep Long-Tailed Learning: A Survey. IEEE Transactions on Pattern Analysis and Machine Intelligence, 45 (9), 10795–10816. https://doi.org/10.1109/tpami.2023.3268118
- Campanella, G., Hanna, M. G., Geneslaw, L., Miraflor, A., Werneck Krauss Silva, V., Busam, K. J. et al. (2019). Clinical-grade computational pathology using weakly supervised deep learning on whole slide images. Nature Medicine, 25 (8), 1301–1309. https://doi.org/10.1038/s41591-019-0508-1
- Jose, L., Liu, S., Russo, C., Nadort, A., Di Ieva, A. (2021). Generative Adversarial Networks in Digital Pathology and Histopathological Image Processing: A Review. Journal of Pathology Informatics, 12 (1), 43. https://doi.org/10.4103/jpi.jpi_103_20
- Saad, M. M., O’Reilly, R., Rehmani, M. H. (2024). A survey on training challenges in generative adversarial networks for biomedical image analysis. Artificial Intelligence Review, 57 (2). https://doi.org/10.1007/s10462-023-10624-y
- Dhariwal, P., Nichol, A. (2021). Diffusion models beat GANs on image synthesis. arXiv:2105.05233. https://doi.org/10.48550/arXiv.2105.05233
- Rombach, R., Blattmann, A., Lorenz, D., Esser, P., Ommer, B. (2022). High-Resolution Image Synthesis with Latent Diffusion Models. 2022 IEEE/CVF Conference on Computer Vision and Pattern Recognition (CVPR), 10674–10685. https://doi.org/10.1109/cvpr52688.2022.01042
- Radford, A., Kim, J. W., Hallacy, C., Ramesh, A., Goh, G., Agarwal, S. et al. (2021). Learning transferable visual models from natural language supervision. arXiv:2103.00020. https://doi.org/10.48550/arXiv.2103.00020
- Chen, R. J., Ding, T., Lu, M. Y., Williamson, D. F. K., Jaume, G., Song, A. H. et al. (2024). Towards a general-purpose foundation model for computational pathology. Nature Medicine, 30, 850–862. https://doi.org/10.1038/s41591-024-02857-3
- Yellapragada, S., Graikos, A., Prasanna, P., Kurc, T., Saltz, J., Samaras, D. (2024). PathLDM: Text conditioned Latent Diffusion Model for Histopathology. 2024 IEEE/CVF Winter Conference on Applications of Computer Vision (WACV), 5170–5179. https://doi.org/10.1109/wacv57701.2024.00510
- Graikos, A., Yellapragada, S., Le, M.-Q., Kapse, S., Prasanna, P., Saltz, J., Samaras, D. (2024). Learned Representation-Guided Diffusion Models for Large-Image Generation. 2024 IEEE/CVF Conference on Computer Vision and Pattern Recognition (CVPR), 8532–8542. https://doi.org/10.1109/cvpr52733.2024.00815
- Boada, J. C., Umer, R. M., Marr, C. (2025). CytoDiff: AI-Driven Cytomorphology Image Synthesis for Medical Diagnostics. 2025 IEEE/CVF International Conference on Computer Vision Workshops (ICCVW), 1136–1144. https://doi.org/10.1109/iccvw69036.2025.00122
- Hu, E. J., Shen, Y., Wallis, P., Allen-Zhu, Z., Li, Y., Wang, S. et al. (2022). LoRA: low-rank adaptation of large language models. arXiv:2106.09685. https://doi.org/10.48550/arXiv.2106.09685
- Ho, J., Jain, A., Abbeel, P. (2020). Denoising diffusion probabilistic models. Proceedings of the 34th International Conference on Neural Information Processing Systems, 34, 6840–6851. https://doi.org/10.48550/arXiv.2006.11239
- Yellapragada, S., Graikos, A., Triaridis, K., Prasanna, P., Gupta, R., Saltz, J., Samaras, D. (2025). ZoomLDM: Latent Diffusion Model for multi-scale image generation. 2025 IEEE/CVF Conference on Computer Vision and Pattern Recognition (CVPR), 23453–23463. https://doi.org/10.1109/cvpr52734.2025.02184
- Mao, Y., Li, H., Pang, W., Papanastasiou, G., Yang, G., Wang, C. (2024). SeLoRA: self-expanding low-rank adaptation of latent diffusion model for medical image synthesis. arXiv:2408.07196. https://doi.org/10.48550/arXiv.2408.07196
- Berezsky, O., Melnyk, G., Liashchynskyi, P., Pitsun, O.; Babichev, S., Lytvynenko, V. (Eds.) (2025). Biomedical Image Datasets. Lecture Notes on Data Engineering and Communications Technologies, vol 244. Cham: Springer, 61–82. https://doi.org/10.1007/978-3-031-88483-2_3
- Berezsky, O., Liashchynskyi, P., Melnyk, G., Dombrovskyi, M., Berezkyi, M. (2024). Synthesis of biomedical images based on generative intelligence tools. Proceedings of the 7th International Conference on Informatics & Data-Driven Medicine (IDDM 2024). Birmingham. CEUR Workshop Proceedings, 3892, 349–362. Available at: https://ceur-ws.org/Vol-3892/paper23.pdf
- Berezsky, O., Liashchynskyi, P., Pitsun, O., Izonin, I. (2024). Synthesis of Convolutional Neural Network architectures for biomedical image classification. Biomedical Signal Processing and Control, 95, 106325. https://doi.org/10.1016/j.bspc.2024.106325
- Berezsky, O., Liashchynskyi, P., Pitsun, O., Melnyk, G. (2024). Method and Software Tool for Generating Artificial Databases of Biomedical Images Based on Deep Neural Networks. 6th International Conference on Informatics & Data-Driven Medicine Bratislava. https://doi.org/10.48550/arXiv.2405.16119
- Kuzmin, S., Berezsky, O. (2025). Analysis of diffusion models and biomedical image generation tools. Computer Systems and Information Technologies, 2, 8–19. https://doi.org/10.31891/csit-2025-2-1
- Zhu, C., Chen, W., Peng, T., Wang, Y., Jin, M. (2022). Hard Sample Aware Noise Robust Learning for Histopathology Image Classification. IEEE Transactions on Medical Imaging, 41 (4), 881–894. https://doi.org/10.1109/tmi.2021.3125459
- Ho, J., Salimans, T. (2022). Classifier-free diffusion guidance. arXiv:2207.12598. https://doi.org/10.48550/arXiv.2207.12598
- Heusel, M., Ramsauer, H., Unterthiner, T., Nessler, B., Hochreiter, S. (2017). GANs trained by a two time-scale update rule converge to a local Nash equilibrium. 31st Conference on Neural Information Processing Systems (NIPS 2017). Long Beac. https://doi.org/10.48550/arXiv.1706.08500
- Bińkowski, M., Sutherland, D. J., Arbel, M., Gretton, A. (2018). Demystifying MMD GANs. International Conference on Learning Representations (ICLR). https://doi.org/10.48550/arXiv.1801.01401
##submission.downloads##
Опубліковано
Як цитувати
Номер
Розділ
Ліцензія
Авторське право (c) 2026 Sergii Kuzmin, Oleh Berezsky

Ця робота ліцензується відповідно до Creative Commons Attribution 4.0 International License.
Закріплення та умови передачі авторських прав (ідентифікація авторства) здійснюється у Ліцензійному договорі. Зокрема, автори залишають за собою право на авторство свого рукопису та передають журналу право першої публікації цієї роботи на умовах ліцензії Creative Commons CC BY. При цьому вони мають право укладати самостійно додаткові угоди, що стосуються неексклюзивного поширення роботи у тому вигляді, в якому вона була опублікована цим журналом, але за умови збереження посилання на першу публікацію статті в цьому журналі.








